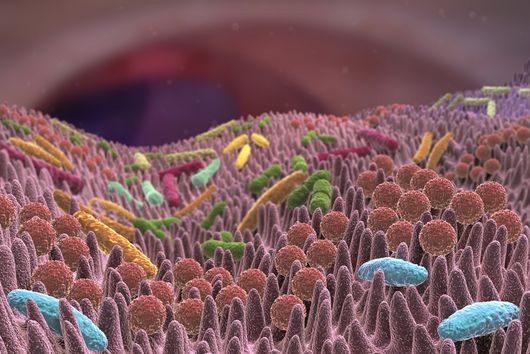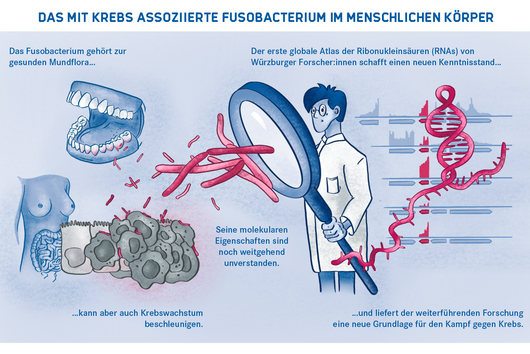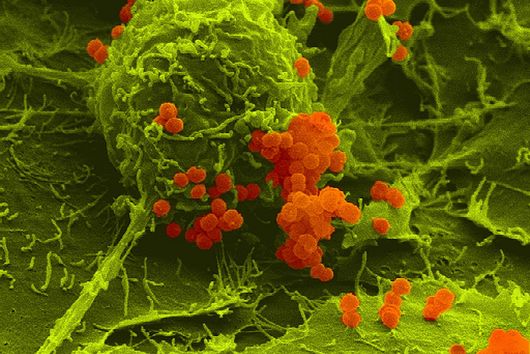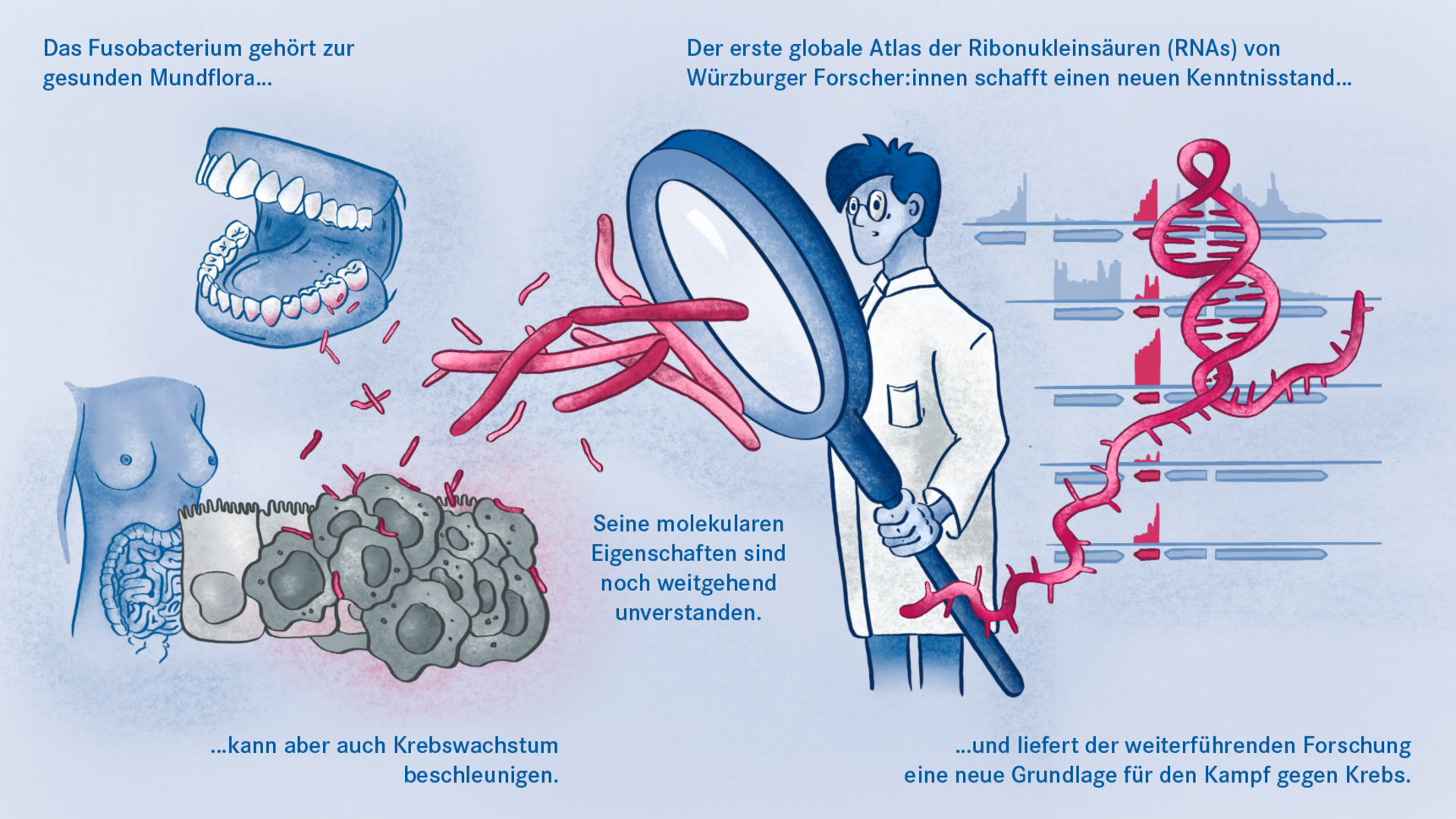
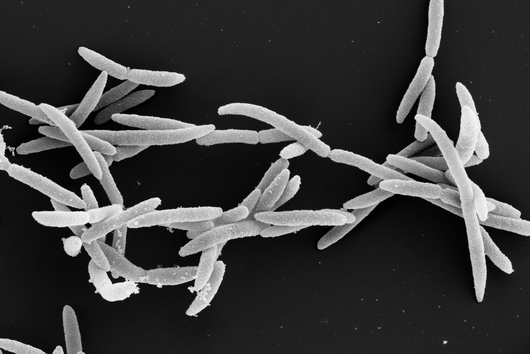
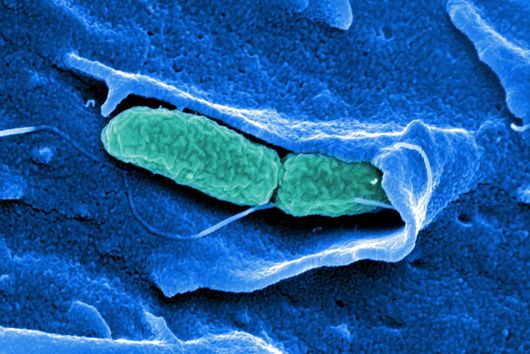
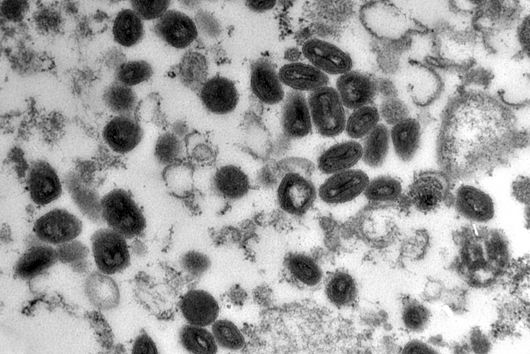
Würzburg, 2. August 2021 – Der Mundhöhlenkeim Fusobacterium nucleatum ist dafür bekannt, das Wachstum menschlicher Karzinome, etwa im Darm oder in der Brust, zu beschleunigen. Das Helmholtz-Institut für RNA-basierte Infektionsforschung (HIRI) und die Julius-Maximilians-Universität (JMU) in Würzburg haben jetzt in einer gemeinsamen Studie die RNA-Moleküle von fünf klinisch relevanten Stämmen dieses anpassungsfähigen Erregers kartiert. Die gewonnenen Erkenntnisse könnten dazu beitragen, neue Therapien bei verschiedenen Krebserkrankungen zu entwickeln. Die Forschungsergebnisse wurden soeben in der Fachzeitschrift Nature Microbiology veröffentlicht.
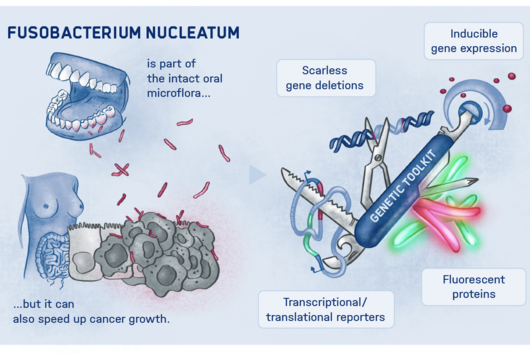
Das Fusobacterium nucleatum kommt in der menschlichen Mundhöhle vor und ist ein wichtiger Bestandteil der gesunden Mundflora. Es kann jedoch auch zur Entstehung von Parodontitis beitragen. Und noch wichtiger: Der Keim wird zunehmend auch innerhalb des menschlichen Körpers, nämlich auf Darmkrebszellen und Mammakarzinomen nachgewiesen. Dort scheint er das Tumorwachstum zu befördern und die Behandlung zu erschweren. Die bisherige Grundlagenforschung hat erste Erkenntnisse über die molekulare Reaktion der Wirtszellen auf die Bakterien erbracht. Weitgehend unverstanden sind bislang jedoch die molekularen Eigenschaften des Erregers selbst, seine Aktivität im Krebsgewebe und wie es ihm gelingt, sich nicht nur im Mund, sondern an ganz unterschiedlichen Stellen im menschlichen Körper anzusiedeln.
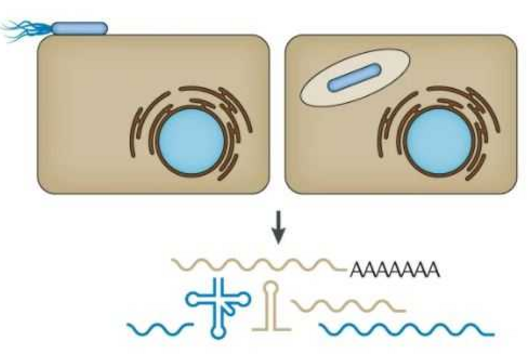
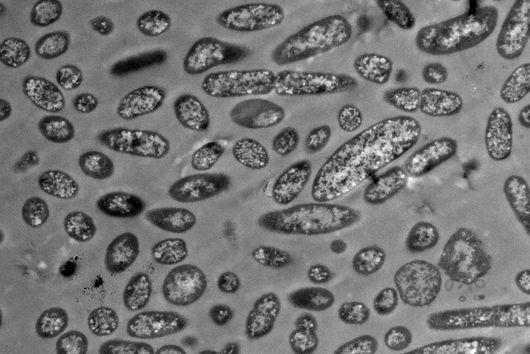
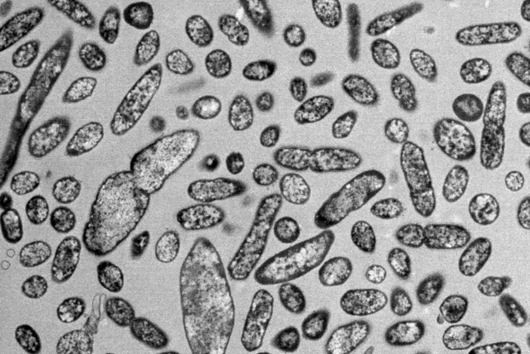
Wissenschaftler:innen vom Helmholtz-Institut für RNA-basierte Infektionsforschung (HIRI) in Würzburg, einem Standort des Braunschweiger Helmholtz-Zentrums für Infektionsforschung (HZI) in Kooperation mit der Julius-Maximilians-Universität Würzburg (JMU), sowie vom Institut für Molekulare Infektionsbiologie (IMIB) der JMU sind bei diesen Fragen jetzt einen entscheidenden Schritt vorangekommen. Sie haben für fünf klinisch relevante Stämme des Keims einen globalen Atlas der RNAs, also der Ribonukleinsäuren (von engl. ribonucleic acid) erstellt. Damit können sie hunderte zuvor unbekannte Ereignisse in der Genregulation der Mikroorganismen nachweisen und zeigen, wie sich diese im Laufe des Bakterienwachstums verändern. Außerdem haben die Forscher:innen erstmals einen Überexpressions-Vektor als genetisches Werkzeug im Fusobacterium eingesetzt, um die Funktionen seines Erbguts zu untersuchen.
RNA-basierter Ansatz eröffnet neue Möglichkeiten
„Unser RNA-basierter Ansatz eröffnet völlig neue Möglichkeiten, einen klinisch überaus relevanten Mikroorganismus auf molekularbiologischer Ebene zu analysieren und besser zu verstehen“, meint HIRI-Direktor Jörg Vogel. Der Professor und zugleich Direktor des IMIB ist Initiator der aktuellen Studie und zuversichtlich, dass die vorliegenden Erkenntnisse die weiterführende translationale, also auf die medizinische Anwendung zielende Forschung befördern werden.

Hintergrund
Die durchgeführte RNA-Kartierung umfasst Fusobacterium nucleatum mit seinen Unterarten nucleatum, animalis, polymorphum und vincentii sowie Fusobacterium periodonticum. Die Wissenschaftler:innen haben die primären Transkriptome – die Gesamtheit der RNA-Moleküle – dieser Stämme erfasst. Um deren genetische Funktionen zu untersuchen, setzte das Team einen Überexpressions-Vektor ein. Das ist gewissermaßen ein Werkzeug, das ein bestimmtes Gen dauerhaft „anschalten“ kann, um dessen Wirkweise genau zu analysieren.
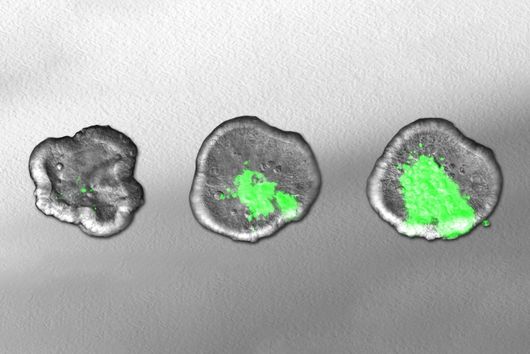
Die Forscher:innen entdeckten durch Einsatz des Überexpressions-Vektors kleine regulatorische RNAs, sogenannte sRNAs (von engl. small RNAs), und konnten erstmals nachweisen, dass diese auch eine regulatorische Funktion in den Mikroorganismen erfüllen. Eine durchaus interessante Beobachtung, wie Falk Ponath, Erstautor der Studie, meint: „Fusobacterium nucleatum hat sich in seiner evolutionsbiologischen Entwicklung recht früh von anderen Bakterien entfernt. Deswegen sind wir nicht von vornherein davon ausgegangen, in den untersuchten Stämmen sRNA zu entdecken, die ähnlich agiert wie bereits bekannte in anderen Bakterien.“ Und nicht nur das: Das Team konnte ebenso nachweisen, dass diese kleine RNA ein Protein der äußeren Zellmembran reguliert.
Die Studienergebnisse untermauerten außerdem die Anpassungsfähigkeit des Keims und könnten zumindest in Teilen erklären, warum dieser als Generalist auftrete, so Ponath. „Der opportunistische Erfolg von Fusobacterium nucleatum im Krebsgewebe ist wahrscheinlich darauf zurückzuführen, dass diejenigen Gene stets aktiv sind, die für die Adhäsion an die Tumorzellen verantwortlich sind“, sagt der Wissenschaftler.
Erstes Fellowship der Vogel-Stiftung Dr. Eckernkamp
Die in der Fachzeitschrift Nature Microbiology veröffentlichte Studie wurde aus Mitteln des Gottfried Wilhelm Leibniz-Preises der Deutschen Forschungsgemeinschaft, verliehen 2017 an Jörg Vogel, sowie durch das Fellowship-Programm der Vogel-Stiftung Dr. Eckernkamp finanziert. Deren Vorstandsvorsitzender Gunther Schunk, Förderer von Fellow Falk Ponath, betont das Stiftungsziel, exzellente wissenschaftliche Arbeit zu unterstützen: „Das HIRI zählt mit seiner RNA-basierten Infektionsforschung zur Weltspitze. Mit den jetzt vorliegenden Studienergebnissen aus unserem Fellowship-Programm, das wir mit der HIRI-Förderung initiiert haben, setzen wir gemeinsam ein starkes Signal in der Grundlagenforschung und im Kampf gegen Krebs“, freut sich Schunk.
Für die künftige Therapie von Krebserkrankungen stellt die Kartografierung des Fuso-Transkriptoms eine wichtige Grundlage dar. Auf ihrer Basis könnten in einem nächsten Schritt Gene identifiziert werden, auf die eine Behandlung zielen kann, um das Fusobacterium in Karzinomen zu beseitigen und das Krebswachstum einzudämmen.
Publikation
RNA landscape of the emerging cancer-associated microbe Fusobacterium nucleatum. Falk Ponath, Caroline Tawk, Yan Zhu, Lars Barquist, Franziska Faber, and Jörg Vogel. Nature Microbiology, 08.07.2021.

Pressekontakt




















![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/b/9/csm_Jahresrueckblick_2025_963859644e.jpg)








![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/e/6/csm_2025_11_20_Neubaufuehrung_fuer_Mitarbeitende_c_HIRI_Yara_Huisl_06_low_0cac9755ff.jpg)
















































![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/5/4/csm_2024_10_EUREKA__c_HIRI_Luisa_Macharowsky_3_low_01_863006bd0e.jpg)































![[Translate to German:]](/fileadmin/HIRI/__processed__/3/3/csm_2022_07_BEISEL_Chase_2_cropped_Low_a7a341cf03.jpg)





































![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/2/8/csm_Collage_WUE_9fa1cd516c.jpg)










![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/0/8/csm_05_Saliba_02_c_HIRI_Luisa_Macharowsky_ohne_Lacoste_low_zugeschnitten_2_01_9822d73a3f.jpg)






![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/c/c/csm_HIRI-Grundstseinlegung_Foto__c_Mario_Schmitt_79ad64af6d.jpg)













![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/c/2/csm_2023_04_Smyth_Paper_c_HIRI_Luisa_Macharowsky_2_low_84f993d581.jpg)





























![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/e/2/csm_2022_11_HIRI_City_of_Wuerzburg_Child_Care_c_HIRI_Luisa_Macharowsky_2_low_6445b253eb.jpg)
![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/3/9/csm_HIRI_key_visual_CHurtig_606d992d74.jpg)





























![[Translate to German:] [Translate to German:]](/fileadmin/HIRI/__processed__/f/0/csm_Ahsen_blue2_6e28a4ee6b.jpg)












![[Translate to Deutsch:] [Translate to Deutsch:]](/fileadmin/HIRI/__processed__/a/5/csm_2022_02_Marco_Olguin_HIRI-Luisa_Macharowsky_04_low_new_3dc837191c.jpg)


![[Translate to Deutsch:] [Translate to Deutsch:]](/fileadmin/HIRI/__processed__/3/c/csm_Joerg_Vogel_Portrait_-_photocredit_Mario_Schmitt__c__HIRI_5013b9643b.jpg)



![[Translate to Deutsch:] [Translate to Deutsch:]](/fileadmin/HIRI/__processed__/a/6/csm_RNA_Delivery_1902376336.jpg)
![[Translate to Deutsch:]](/fileadmin/HIRI/__processed__/7/c/csm_Caliskan_Kibe_Pekarek_105c7d1860.jpg)
![[Translate to Deutsch:] [Translate to Deutsch:]](/fileadmin/HIRI/__processed__/c/1/csm_N-Caliskan_M-Zimmer_Zoom_c93c493293.jpg)